传统的基因敲除法对于没有基因注释,缺乏功能信息的基因来说,有很大的限制。Tn-seq是高通量测序与传统的转座子诱变相结合的转座子测序技术,可以利用高通量的方法获得与所研究表型相关的未知基因。
来自Northeastern University生物系的Edware Geisinger团队在Nature Communication上发表的该文章使用Tn-seq技术来鉴定与鲍曼不动杆菌对多种抗生素敏感性相关的基因。通过鉴定多种抗生素敏感性相关突变体的突变基因,他们推断出了多个未表征过的蛋白的功能,并用实验进行验证。
Tn-seq测序:Tn-seq技术可以通过转座子随机插入突变的方法获得突变体库,利用表型筛选实验筛选出具有某一表型的突变体库,再通过高通量测序获得插入突变位点的DNA序列,再最终将表型、基因型、突变频率等对应起来,从而鉴定出与表型相关的基因,或推断突变基因的功能。
研究思路
1)使用Tn10和mariner两种类型的转座子,对鲍曼不动杆菌的标准菌株ATCC 17978进行转座子随机诱变。
2)分别添加低于MIC浓度(sub-MIC)的20种抗生素进行培养。低浓度抗生素的使用会使菌株存活率与无抗生素环境相比降低20%-30%。
3)将使用该抗生素前后的菌株DNA进行提取测序,最后通过每个基因的突变丰度来鉴定该抗生素的相关基因,最后得到了特征基因在多种抗生素中的突变适应度(fitness);
4)研究发现了一些与抗生素作用相关的未知功能的保守基因,尤其是发现了与细胞被膜合成相关基因与抗生素的相关性,并对发现基因的功能进行了实验验证。
实验结果:
1. 进行Tn-seq测序分析,总共筛选出了327个基因与至少一种抗生素相关,其中245个基因的突变适应度降低,122个基因的突变适应度增高,这些基因作为候选基因进行下一步研究。抗生素敏感性特征可用于鉴定鲍曼不动杆菌不同基因之间的功能关系。例如细胞分裂相关蛋白和DNA重组修复蛋白的适应性特征相似,都对攻击细胞壁和破坏DNA的抗生素具有一致的超敏反应。
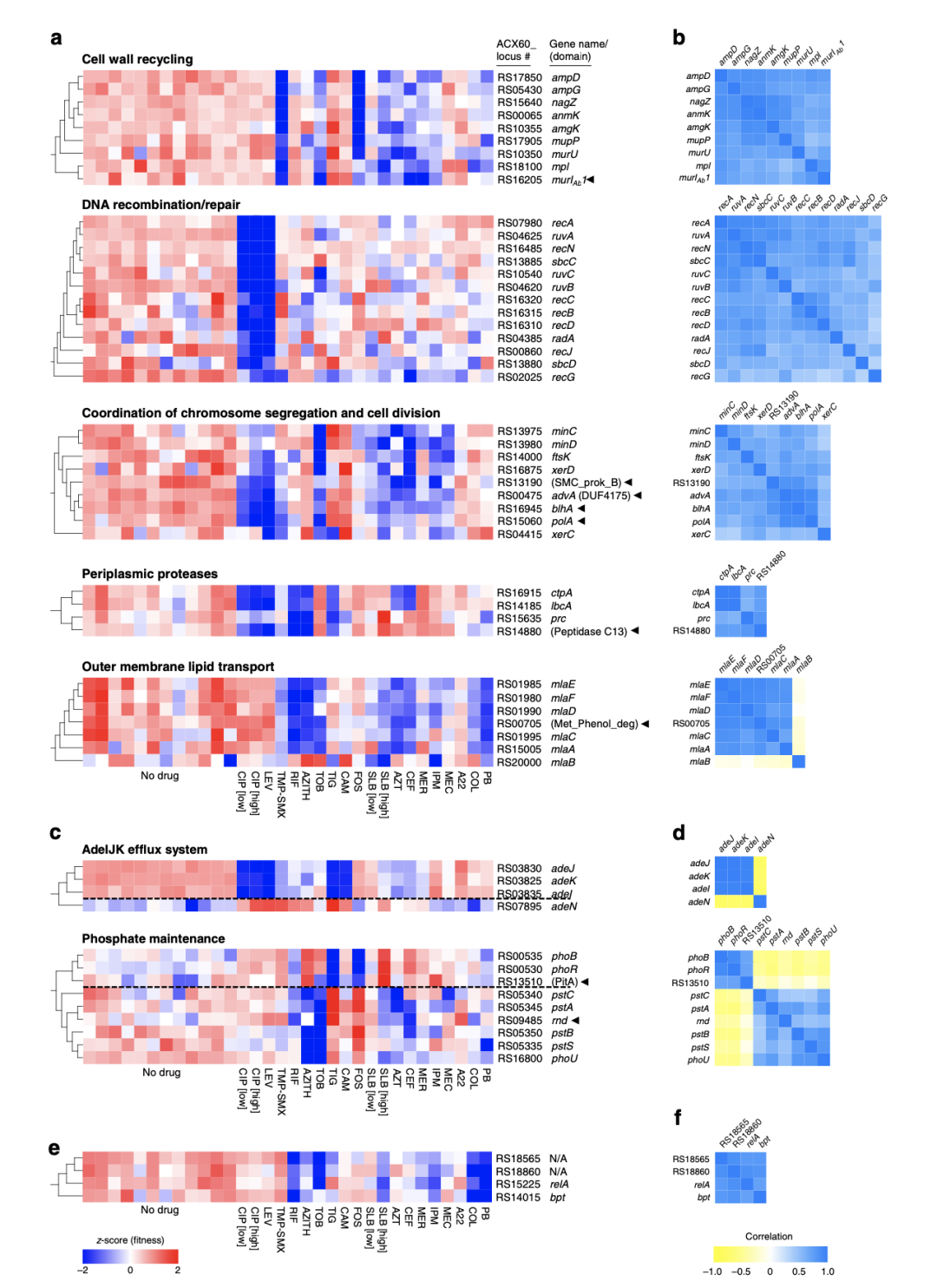 图
图
2. 与染色体复制/分离,细胞分裂活动相关的一系列基因在其Tn-seq适应度(fitness)特征中显示出相似性,其中包含有没被注释过的基因ACX60_RS00475,被命名为 AdvA基因。并且进一步通过实验验证了AdvA基因的作用,以及对奎诺酮药物和beta 内酰胺类抗生素药物的抗药性研究。
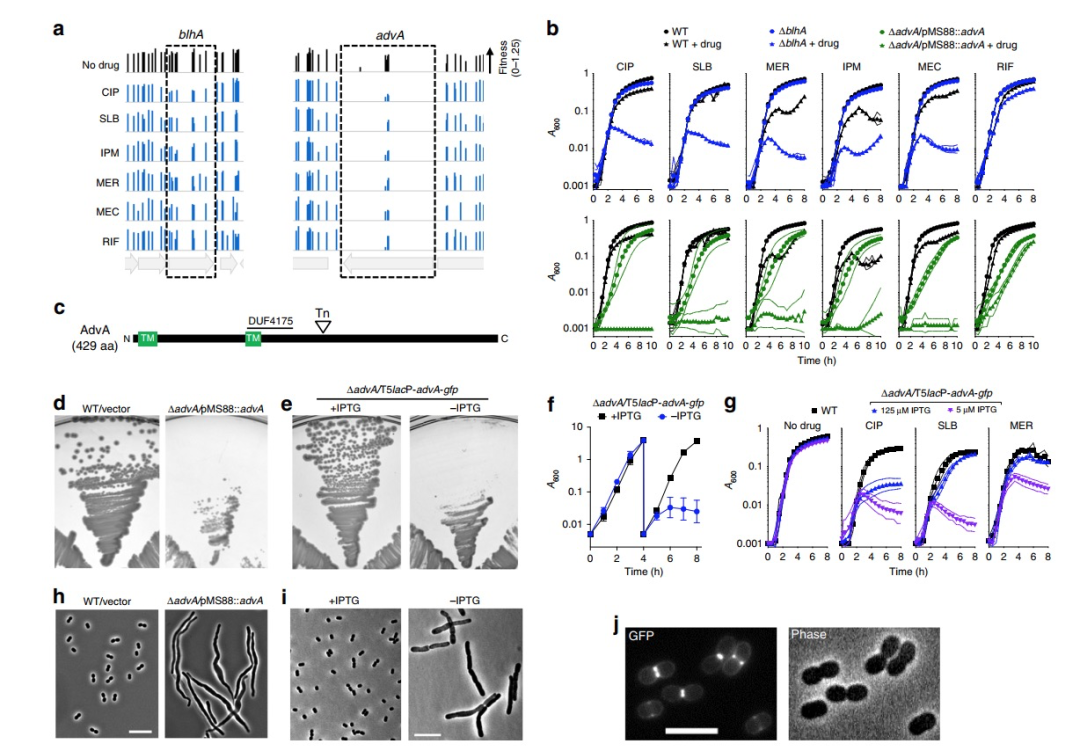 图
图
3. 通过Tn-seq fitness的耐药表型关联性分析,预测出细胞壁水解蛋白pbpG与LOS(lipooligosaccharide, 寡聚糖)相关基因正相关,都对疏水性抗生素药物敏感, 进一步通过实验验证了pbpG蛋白的敲除会导致LOS的减少。
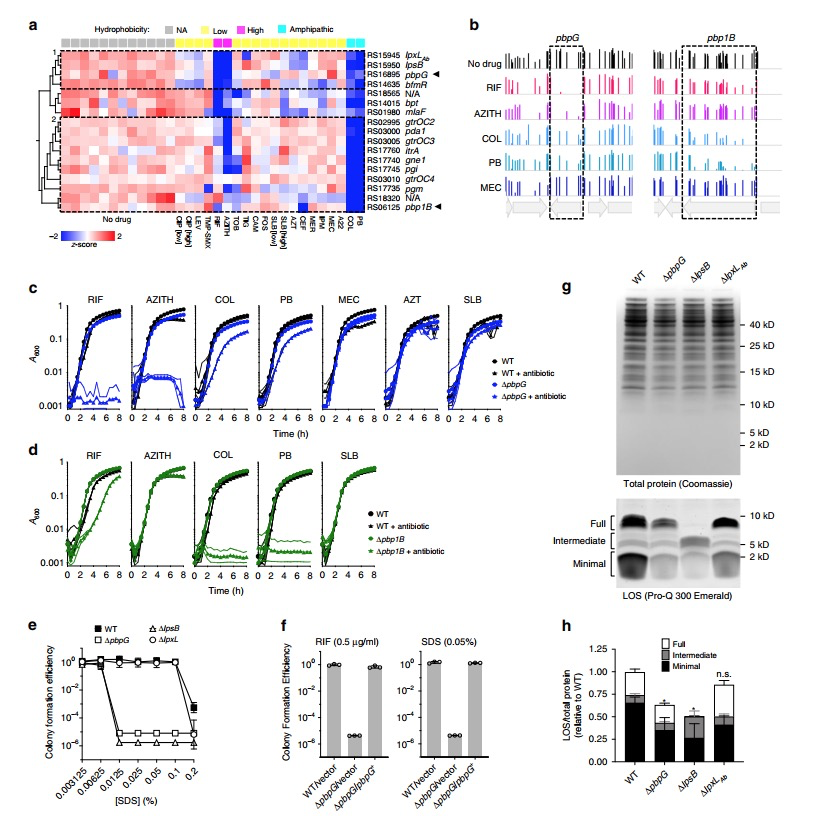 图
图
4. 对敏感性特征和抗生素诱导的形态学模式的相关性分析给我们预测药物的协同作用提供理论基础。
原文链接:
https://pubmed.ncbi.nlm.nih.gov/32908144/
本文来源:血流感染细菌监测BRICS